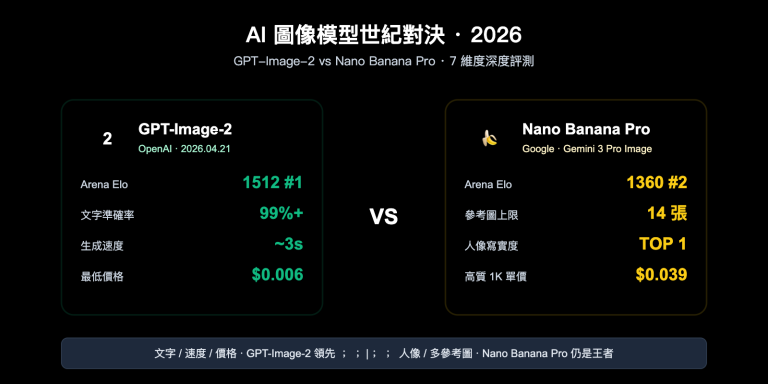
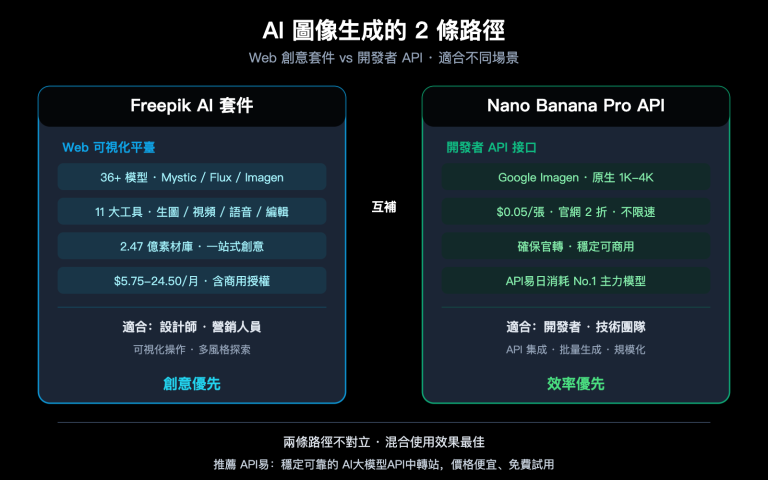
作者注:詳解如何用 Nano Banana 2 生成符合 Nature、Science、Cell 等頂級期刊要求的科研插圖,包含 7 個提示詞技巧、5 類圖表模板和完整 API 調用代碼

科研論文中,一張高質量的 Figure 往往決定了審稿人的第一印象。傳統科研繪圖依賴 BioRender、Adobe Illustrator 等工具,學習曲線陡峭且費用不菲。
現在,Nano Banana 2 憑藉內建的科學知識推理能力和精準文字渲染,正在成爲科研工作者的新選擇。從信號通路圖到 Graphical Abstract,從實驗流程圖到數據可視化,一段提示詞就能生成接近出版級質量的科研插圖。
核心價值: 讀完本文,你將掌握 7 個科研繪圖提示詞技巧,獲得 5 類頂刊圖表的提示詞模板,並學會通過 API 批量生成和迭代優化科研插圖的完整工作流。
Nano Banana 2 科研繪圖 核心要點
| 要點 | 說明 | 價值 |
|---|---|---|
| 科學知識內建 | 基於 Gemini 3 架構,理解生物、化學、物理等學科概念 | 無需手動標註每個組件 |
| 文字渲染 97%+ | 英文標註幾乎完美,支持多語言文字渲染 | 基因名、蛋白名、化學式準確呈現 |
| 4K 超高分辨率 | 原生支持 4096px 輸出,滿足 300 DPI 要求 | 直接達到頂刊投稿分辨率標準 |
| 多輪對話編輯 | 支持迭代修改,逐步調整細節 | 適合科研繪圖的精細打磨流程 |
| 成本極低 | 單張 $0.045,迭代 10 次不到 $0.5 | 相比 BioRender $15/月訂閱大幅節省 |
Nano Banana 2 科研繪圖的核心優勢
Nano Banana 2(Gemini 3.1 Flash Image Preview)與傳統繪圖工具最大的區別在於,它不只是一個「畫圖工具」,而是一個理解科學概念的繪圖引擎。當你輸入「MAPK/ERK signaling pathway with RAS activation」時,它能基於 Gemini 的知識庫正確理解 RAS→RAF→MEK→ERK 的級聯關係,自動生成合理的通路圖佈局,而不是簡單地畫幾個方塊和箭頭。
這種「知識驅動」的生成方式對科研繪圖至關重要——它意味着你可以把更多精力放在科學敘事的設計上,而不是糾結於每個組件的位置和連線。
Nano Banana 2 科研繪圖的適用邊界
需要明確的是,AI 生成的科研插圖目前更適合作爲快速原型和基礎版本,最終投稿級別的 Figure 通常需要在 Illustrator 或 Photoshop 中做精細調整。推薦工作流是:Nano Banana 2 快速生成 → 人工校驗科學準確性 → 專業工具精修導出。
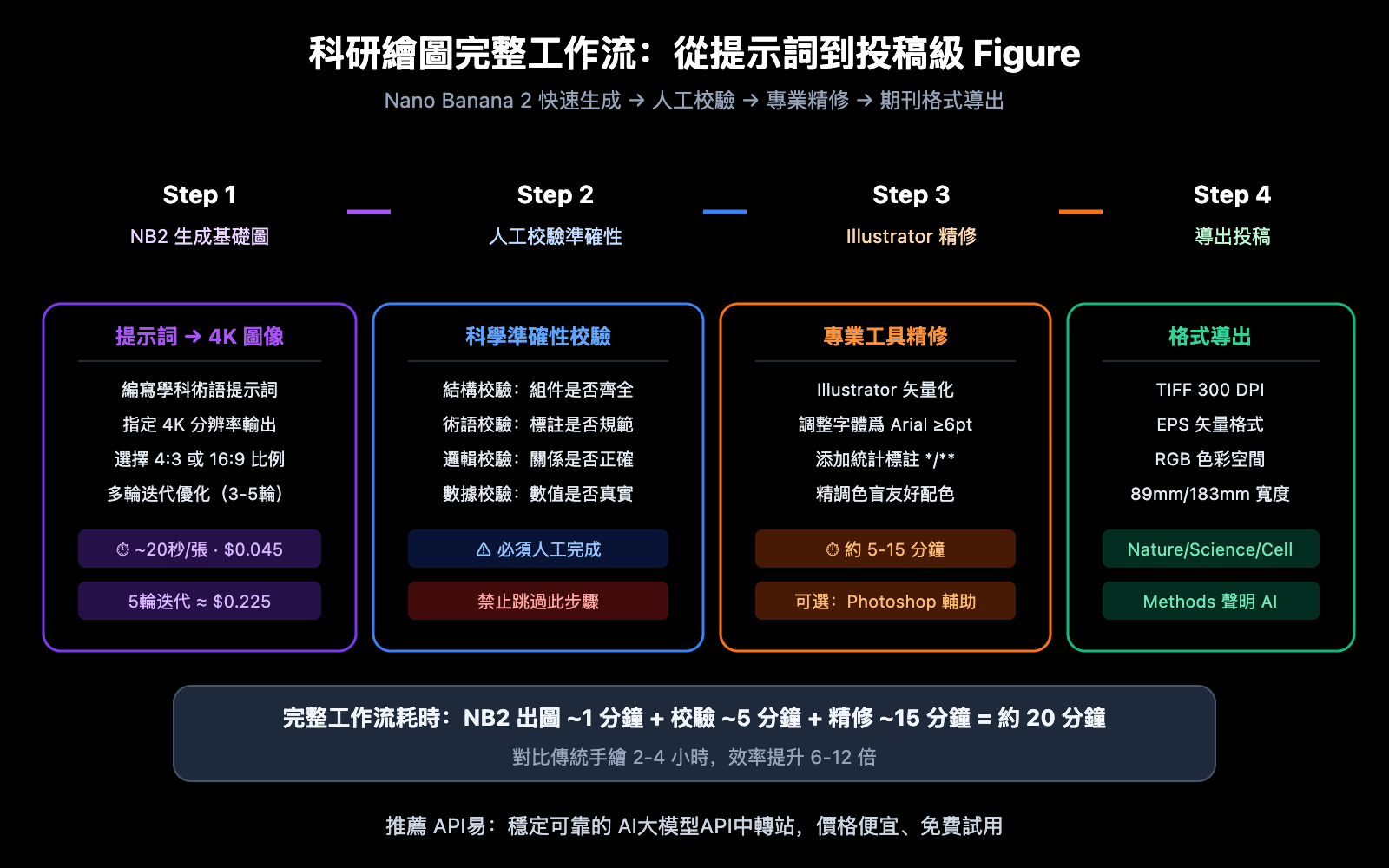
Nano Banana 2 科研繪圖 7 個提示詞技巧
以下 7 個技巧是科研繪圖提示詞的核心方法論,適用於所有類型的科研插圖。
技巧 1:使用精準學科術語
科研繪圖的提示詞必須使用標準化的學科術語,而不是通俗描述。Nano Banana 2 基於 Gemini 的知識庫能正確理解專業術語,並生成學術規範的圖表。
| 通俗描述(效果差) | 學科術語(效果好) | 適用領域 |
|---|---|---|
| 細胞信號傳遞過程 | MAPK/ERK signaling cascade with phosphorylation events | 分子生物學 |
| DNA 複製的圖 | Semi-conservative DNA replication fork with leading and lagging strand | 遺傳學 |
| 藥物作用機制 | Pharmacokinetic ADME pathway diagram | 藥理學 |
| 蛋白質結構 | Protein tertiary structure with alpha-helix and beta-sheet domains | 結構生物學 |
| 化學反應過程 | SN2 nucleophilic substitution reaction mechanism with transition state | 有機化學 |
提示詞示例:
Create a scientific schematic of the PI3K/AKT/mTOR signaling pathway.
Include: receptor tyrosine kinase activation, PI3K recruitment,
PIP2 to PIP3 conversion, AKT phosphorylation at Thr308 and Ser473,
mTORC1 and mTORC2 complexes, downstream targets S6K1 and 4E-BP1.
Use standard molecular biology iconography.
Arrows indicate activation, flat-headed lines indicate inhibition.
Clean white background, publication-quality, 4K resolution.
技巧 2:指定出版級別格式參數
不同頂刊對 Figure 有嚴格的格式要求。在提示詞中直接指定這些參數,可以減少後期調整的工作量。
| 期刊 | 單欄寬度 | 雙欄寬度 | 最低 DPI | 推薦格式 | 字體要求 |
|---|---|---|---|---|---|
| Nature | 89mm | 183mm | 300 DPI | TIFF/EPS | Arial/Helvetica ≥6pt |
| Science | 85mm | 174mm | 300 DPI | EPS/PDF | Helvetica ≥6pt |
| Cell | 85mm | 174mm | 300 DPI | TIFF/PDF | Arial ≥6pt |
| Elsevier | 90mm | 190mm | 300-1000 DPI | TIFF/EPS | Arial ≥8pt |
| PLOS ONE | 83mm | 173mm | 300 DPI | TIFF/PNG | Arial/Helvetica ≥8pt |
格式參數後綴(追加到任意科研繪圖提示詞末尾):
Output specifications: 4K resolution (4096px width),
white or light gray background,
Arial font family, minimum 8pt text size,
RGB color mode, high contrast,
clean layout with adequate white space,
suitable for Nature/Science journal submission
技巧 3:多輪對話迭代修改
科研繪圖很少一次生成就完美。Nano Banana 2 支持多輪對話編輯,你可以在上一輪結果的基礎上逐步調整。
迭代修改策略:
- 第 1 輪:生成基本結構和佈局
- 第 2 輪:調整標註文字的大小和位置
- 第 3 輪:優化顏色方案,確保色盲友好
- 第 4 輪:精修細節,對齊元素間距
每輪只修改一個方面,避免一次提出過多修改導致模型混亂。例如:
Round 1: "Create a schematic of CRISPR-Cas9 gene editing mechanism..."
Round 2: "Make the guide RNA label larger, move it to the upper right"
Round 3: "Change the Cas9 protein color from blue to teal (#0d9488)"
Round 4: "Add a scale bar and increase spacing between PAM site label and the DNA"
技巧 4:指定學術配色規範
科研插圖的配色需要遵循學術規範,同時確保色盲友好(約 8% 的男性存在紅綠色盲)。
推薦學術配色方案:
Color scheme for scientific figure:
- Activation/positive: green (#10b981 to #34d399)
- Inhibition/negative: red (#ef4444 to #f87171)
- Neutral pathways: blue (#3b82f6 to #60a5fa)
- Highlighted element: orange (#f97316 to #fb923c)
- Background structures: gray (#94a3b8 to #cbd5e1)
Ensure colorblind accessibility (deuteranopia-safe).
Use hatching patterns as secondary visual encoding.
色盲友好原則:避免僅依靠紅綠區分信息,使用藍橙對比替代紅綠對比,同時疊加形狀或紋理作爲輔助編碼。
技巧 5:分模塊生成複雜 Figure
頂刊論文的 Figure 通常包含多個 Panel(A、B、C、D),一次性生成複雜多面板圖容易導致佈局混亂。推薦分模塊生成後再用 Illustrator 組合。
多面板 Figure 提示詞模板:
Generate Panel [A/B/C/D] of a multi-panel scientific figure:
Panel content: [具體內容描述]
Panel size: 85mm x 85mm (square format)
Panel label: Bold letter "[A]" in top-left corner, 12pt Arial
Consistent color scheme: [配色說明]
White background, 4K resolution, clean borders
Leave 5mm margin on all sides for assembly
技巧 6:利用參考圖提升準確性
Nano Banana 2 支持上傳最多 14 張參考圖片。對於科研繪圖,上傳已發表論文中類似的 Figure 作爲風格參考,可以顯著提升輸出的學術風格一致性。
參考圖使用方法:
- 上傳 1-2 張目標期刊中類似主題的已發表 Figure
- 在提示詞中說明
Follow the visual style and layout of the reference figure - 明確指出需要保留的元素和需要更改的內容
技巧 7:添加統計標註和圖例
科研 Figure 通常需要統計標註(如顯著性星號 、、)和圖例。目前 AI 生成這些精細標註的準確率有限,建議在提示詞中預留空間。
Leave space in the upper-right corner for a legend box (approximately 25mm x 15mm).
Leave space above each bar for statistical significance markers.
Do not generate placeholder statistics - I will add real p-values manually.
🎯 實戰建議: 統計標註建議在後期用 Illustrator 手動添加,確保數值準確。通過 API易 apiyi.com 平臺調用 Nano Banana 2 快速生成基礎圖後,在專業工具中完成最終精修。
Nano Banana 2 科研繪圖 5 類圖表模板
以下 5 類模板覆蓋科研論文中最常見的 Figure 類型,直接複製提示詞即可使用。
模板 1:信號通路機制圖(Pathway Diagram)
適用於分子生物學、細胞生物學、藥理學等領域。
Create a publication-quality schematic diagram of [PATHWAY NAME].
Components to include:
- [Receptor/protein 1] at the cell membrane
- [Kinase cascade: A → B → C → D]
- [Transcription factor] translocation to nucleus
- [Target gene] activation
Visual specifications:
- Cell membrane as a phospholipid bilayer at the top
- Cytoplasm in light beige, nucleus in light blue
- Activation arrows: solid green (#10b981), 2pt weight
- Inhibition lines: flat-headed red (#ef4444), 2pt weight
- Protein nodes: rounded rectangles with gradient fill
- All labels in Arial 10pt, black text on white background boxes
- White background, 4K resolution
- Style: Nature Reviews Molecular Cell Biology
模板 2:Graphical Abstract(圖形摘要)
頂刊越來越多地要求提交 Graphical Abstract,用一張圖概括研究核心發現。
Create a Graphical Abstract for a research paper about [RESEARCH TOPIC].
Layout: left-to-right narrative flow, 3 main sections
- Left section: [Input/Problem/Starting material]
- Center section: [Method/Process/Intervention]
- Right section: [Output/Result/Discovery]
Connect sections with bold directional arrows.
Use icons and simplified illustrations rather than text.
Minimal text labels, maximum 15 words total.
Color palette: [primary color] for main elements, [accent color] for highlights.
Size: landscape orientation, 16:9 aspect ratio.
Clean white background, modern flat design style.
4K resolution, suitable for Cell/Nature submission.
模板 3:實驗流程圖(Experimental Workflow)
適用於 Methods 部分的實驗流程說明。
Create a step-by-step experimental workflow diagram for [EXPERIMENT NAME].
Steps (left to right or top to bottom):
1. [Step 1: Sample preparation - brief description]
2. [Step 2: Treatment/Processing - brief description]
3. [Step 3: Analysis method - brief description]
4. [Step 4: Data collection - brief description]
5. [Step 5: Results - brief description]
Visual style:
- Each step as a rounded rectangle with icon
- Connected by arrows with brief condition labels (e.g., "37°C, 24h")
- Timeline or duration indicators between steps
- Color-coded by phase: preparation (blue), experiment (green), analysis (purple)
- Clean white background, Arial font, 4K resolution
- Publication-ready for supplementary materials
模板 4:對比結果圖(Comparison Figure)
適用於不同實驗條件或方法的對比展示。
Create a scientific comparison figure showing [COMPARISON TOPIC].
Layout: side-by-side comparison, 2-3 conditions
- Condition A: [Control group description]
- Condition B: [Treatment group description]
- Condition C (optional): [Alternative treatment]
Include:
- Representative images/schematics for each condition
- Consistent scale and orientation across conditions
- Condition labels at the top (bold, 12pt)
- Key differences highlighted with colored annotations
- Scale bar in bottom-right corner
- White background, 4K resolution, Nature-style layout
模板 5:數據可視化概念圖(Data Visualization Concept)
適用於複雜數據關係的概念性可視化(注意:精確數據圖仍需 Python/R 生成)。
Create a conceptual data visualization diagram showing [DATA RELATIONSHIP].
Visualization type: [heatmap concept / network diagram / Venn diagram / scatter plot concept]
Key elements:
- [X-axis/Category 1]: [description]
- [Y-axis/Category 2]: [description]
- [Data trend/Pattern]: [description]
Style:
- Clean minimalist design
- Color gradient: [low value color] to [high value color]
- Clear axis labels and title
- Legend in top-right corner
- White background, 4K resolution
Note: This is a conceptual illustration. Real data plots should be generated with matplotlib/R.
💡 重要提醒: Nano Banana 2 擅長生成概念性科研插圖(機制圖、流程圖、Graphical Abstract),但精確的統計圖表(帶真實數據的柱狀圖、散點圖)仍推薦使用 Python matplotlib 或 R ggplot2 生成。AI 生成的數據可視化可能包含不準確的數值,需要嚴格校驗。
Nano Banana 2 科研繪圖 API 快速上手
極簡示例
以下代碼通過 API易 平臺調用 Nano Banana 2 生成一張科研信號通路圖:
import requests, base64
API_KEY = "your-apiyi-api-key"
ENDPOINT = "https://api.apiyi.com/v1beta/models/gemini-3.1-flash-image-preview:generateContent"
prompt = """Create a publication-quality schematic of the Wnt/beta-catenin signaling pathway.
Include: Wnt ligand, Frizzled receptor, Dishevelled, GSK-3beta destruction complex,
beta-catenin stabilization and nuclear translocation, TCF/LEF transcription.
Activation arrows in green, inhibition in red. White background, Arial font, 4K resolution."""
payload = {
"contents": [{"parts": [{"text": prompt}]}],
"generationConfig": {"responseModalities": ["IMAGE"], "imageConfig": {"aspectRatio": "4:3", "imageSize": "4K"}}
}
response = requests.post(ENDPOINT, headers={"Content-Type": "application/json", "x-goog-api-key": API_KEY}, json=payload, timeout=120)
image_data = response.json()["candidates"][0]["content"]["parts"][0]["inlineData"]["data"]
with open("wnt_pathway.png", "wb") as f:
f.write(base64.b64decode(image_data))
查看多輪迭代修改的完整代碼
import requests
import base64
import json
API_KEY = "your-apiyi-api-key"
ENDPOINT = "https://api.apiyi.com/v1beta/models/gemini-3.1-flash-image-preview:generateContent"
headers = {"Content-Type": "application/json", "x-goog-api-key": API_KEY}
def generate_figure(prompt, filename, aspect_ratio="4:3", size="4K"):
"""生成單張科研插圖"""
payload = {
"contents": [{"parts": [{"text": prompt}]}],
"generationConfig": {
"responseModalities": ["IMAGE"],
"imageConfig": {"aspectRatio": aspect_ratio, "imageSize": size}
}
}
response = requests.post(ENDPOINT, headers=headers, json=payload, timeout=120)
result = response.json()
image_data = result["candidates"][0]["content"]["parts"][0]["inlineData"]["data"]
with open(filename, "wb") as f:
f.write(base64.b64decode(image_data))
print(f"Saved: {filename}")
return result
# ========== 多輪迭代示例 ==========
# Round 1: 生成基礎版本
prompt_r1 = """Create a schematic of CRISPR-Cas9 gene editing mechanism.
Show: guide RNA binding to target DNA, Cas9 protein cutting double-strand,
PAM site recognition, and DNA repair pathways (NHEJ and HDR).
White background, publication quality, 4K resolution."""
generate_figure(prompt_r1, "crispr_v1.png")
# Round 2: 調整標註(傳入上一輪圖片作爲參考)
prompt_r2 = """Based on the previous CRISPR diagram, make these changes:
1. Enlarge the guide RNA label to 12pt bold
2. Add a dashed box around the PAM site region
3. Use blue (#3b82f6) for NHEJ pathway, green (#10b981) for HDR pathway
4. Add small arrow labels for 'Blunt-end joining' and 'Template-directed repair'
Keep all other elements unchanged. 4K resolution."""
# 讀取上一輪圖片作爲參考輸入
import pathlib
prev_image = pathlib.Path("crispr_v1.png").read_bytes()
payload_r2 = {
"contents": [{
"parts": [
{"inlineData": {"mimeType": "image/png", "data": base64.b64encode(prev_image).decode()}},
{"text": prompt_r2}
]
}],
"generationConfig": {
"responseModalities": ["IMAGE"],
"imageConfig": {"aspectRatio": "4:3", "imageSize": "4K"}
}
}
response_r2 = requests.post(ENDPOINT, headers=headers, json=payload_r2, timeout=120)
result_r2 = response_r2.json()
image_r2 = result_r2["candidates"][0]["content"]["parts"][0]["inlineData"]["data"]
with open("crispr_v2.png", "wb") as f:
f.write(base64.b64decode(image_r2))
print("Saved: crispr_v2.png (iteration 2)")
建議: 科研繪圖通常需要 3-5 輪迭代才能達到滿意效果。通過 API易 apiyi.com 調用 Nano Banana 2,按次計費 $0.045/次,5 輪迭代成本僅 $0.225(約 1.6 元),遠低於 BioRender 等專業工具的月費。
Nano Banana 2 科研繪圖 與傳統工具對比

| 對比項 | Nano Banana 2 | BioRender | Adobe Illustrator |
|---|---|---|---|
| 學習成本 | 極低(寫提示詞) | 中等(模板拖拽) | 高(專業軟件) |
| 生成速度 | 5-20 秒/張 | 10-30 分鐘/張 | 1-4 小時/張 |
| 科學準確性 | 中高(需人工校驗) | 高(預設生物組件) | 取決於作者 |
| 文字渲染 | 97%+ 準確率 | 100%(手動輸入) | 100%(手動輸入) |
| 最大分辨率 | 4K(4096px) | 取決於導出設置 | 矢量無限縮放 |
| 中文標註 | 支持(質量中等) | 支持 | 完美支持 |
| 費用 | $0.045/張(API易) | $15-39/月 | $22.99/月 |
| 矢量輸出 | 否(位圖 PNG) | 部分支持 | 完美矢量 |
| 批量生成 | 支持 API 批量 | 不支持 | 不支持 |
| 適合階段 | 快速原型 + 初稿 | 中等複雜度終稿 | 高複雜度終稿 |
🎯 選擇建議: 推薦「Nano Banana 2 + Illustrator」組合工作流:先用 Nano Banana 2 快速生成基礎版本($0.045/張),確認佈局和內容後再導入 Illustrator 做矢量化精修。通過 API易 apiyi.com 平臺調用模型,批量迭代成本極低。
Nano Banana 2 科研繪圖 頂刊投稿注意事項
期刊 AI 圖像政策現狀
頂級期刊對 AI 生成圖像有明確的政策規定,投稿前必須瞭解:
| 期刊 | AI 生成圖像政策 | 披露要求 | 例外情況 |
|---|---|---|---|
| Nature | 原則上不允許 | 必須在 Methods 中聲明 | 基於可溯源科學數據集的 AI 工具可豁免,需標註 |
| Science | 未經編輯許可不允許 | 投稿時聲明 | 研究 AI/ML 的論文可申請例外 |
| Cell | 限制使用 | 必須披露 | Graphical Abstract 和示意圖經披露後可接受 |
| Elsevier | 允許但須披露 | Methods 或致謝部分 | 須標註爲 AI 生成並說明使用的工具 |
| PLOS ONE | 允許但須披露 | Methods 部分 | 須確保準確性並聲明 AI 工具名稱 |
科研繪圖的合規建議
- 始終披露:在 Methods 部分明確寫出「Figure X was generated using Nano Banana 2 (Gemini 3.1 Flash Image Preview, Google DeepMind) and refined in Adobe Illustrator」
- 人工校驗:AI 生成的科研插圖必須由研究者逐一校驗科學準確性,不能盲目信任
- 避免僞造數據:AI 可以生成看起來非常「科學」的假數據圖表,嚴禁將 AI 生成的數據圖充當真實實驗數據
- 保留過程記錄:保存每輪迭代的提示詞和輸出圖片,以備審稿人詢問
常見問題
Q1: Nano Banana 2 生成的科研插圖能直接投稿嗎?
不建議直接投稿。推薦工作流是:Nano Banana 2 生成 4K 基礎圖(約 20 秒)→ 研究者校驗科學準確性 → Illustrator/Photoshop 精修細節(調整標註、添加統計標記、轉矢量)→ 導出目標期刊要求的格式(TIFF/EPS)。同時必須在 Methods 部分聲明使用了 AI 工具。通過 API易 apiyi.com 調用模型快速迭代,每次僅需 $0.045。
Q2: 生成的圖片分辨率能滿足頂刊要求嗎?
Nano Banana 2 最高支持 4K(4096×4096px)輸出。以 Nature 要求的雙欄寬度 183mm、300 DPI 計算,所需像素爲 2165px,4K 輸出完全滿足。但 AI 生成的是位圖(PNG),如果期刊要求矢量格式(EPS/AI),需要在 Illustrator 中使用 Image Trace 轉換。建議通過 API易 apiyi.com 生成 4K 版本,確保分辨率充足。
Q3: 如何保證 AI 生成圖表的科學準確性?
三步校驗法:
- 結構校驗:檢查通路/流程中的每個組件是否存在、關係是否正確
- 術語校驗:檢查所有標註文字是否爲標準學術術語,拼寫是否正確
- 邏輯校驗:檢查箭頭方向、激活/抑制關係、因果鏈是否符合已知科學事實
AI 生成的插圖可能出現「看起來專業但科學上錯誤」的內容,這是最需要警惕的風險。
Q4: 中文標註的效果如何?
Nano Banana 2 對中文文字渲染的質量不如英文穩定,中文標註可能出現字形不完整或間距不均等問題。對於國內期刊投稿,建議在提示詞中先用英文標註生成,然後在 Illustrator 中手動替換爲中文。國際期刊投稿直接使用英文標註即可,準確率 97% 以上。
總結
Nano Banana 2 科研繪圖的核心要點:
- 用學科術語寫提示詞:精準術語是生成質量的關鍵,避免通俗描述
- 4K + 4:3 滿足頂刊標準:原生 4K 輸出覆蓋 Nature/Science/Cell 的 300 DPI 要求
- 多輪迭代精修:每輪只改一個方面,3-5 輪即可接近出版級質量
- AI 生成 + 手動精修的混合工作流:快速出圖用 Nano Banana 2,最終精修用 Illustrator
- 必須披露和校驗:頂刊要求在 Methods 中聲明 AI 工具使用,科學準確性必須人工把關
推薦通過 API易 apiyi.com 平臺調用 Nano Banana 2,單張僅 $0.045,5 輪迭代不到 $0.25。相比 BioRender 訂閱費和傳統手繪的時間成本,是科研繪圖的高效起點。
📚 參考資料
-
Google Nano Banana 2 圖像生成文檔: 官方 API 參數和能力說明
- 鏈接:
ai.google.dev/gemini-api/docs/image-generation - 說明: 包含分辨率、寬高比、Thinking 模式等完整參數說明
- 鏈接:
-
Nature 投稿 Figure 指南: Nature 期刊的圖表格式要求
- 鏈接:
research-figure-guide.nature.com/figures/preparing-figures-our-specifications/ - 說明: 包含分辨率、字體、尺寸等詳細投稿規格
- 鏈接:
-
Nature AI 政策: Nature 對 AI 生成內容的編輯政策
- 鏈接:
nature.com/nature-portfolio/editorial-policies/ai - 說明: 瞭解頂刊對 AI 生成圖像的最新政策要求
- 鏈接:
-
API易 Nano Banana 2 接入文檔: API易平臺的 Nano Banana 2 調用指南
- 鏈接:
docs.apiyi.com/en/api-capabilities/nano-banana-2-image - 說明: 包含按次和按量計費方案,適合科研繪圖的迭代使用
- 鏈接:
作者: APIYI 技術團隊
技術交流: 更多 AI 科研繪圖技巧和學術出版工具推薦,歡迎訪問 API易 docs.apiyi.com 文檔中心